Transcrición xenética
Este artigo contén varias ligazóns externas e/ou bibliografía ao fin da páxina, mais poucas ou ningunha referencia no corpo do texto. Por favor, mellora o artigo introducindo notas ao pé, citando as fontes. Podes ver exemplos de como se fai nestes artigos. |
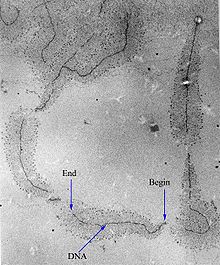
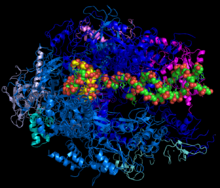



A transcrición é o proceso celular por medio do cal a partir dunha secuencia molde de ADN se realiza unha copia en ARN complementaria en bases a dito ADN.[1] A transcrición é o primeiro paso da expresión xenética, xa que despois o ARN formado será traducido a proteínas, aínda que non todos os transcritos de ARN son traducidos. Non se transcribe o ADN enteiro, senón só xenes concretos en cada momento.
ARN e ADN son ácidos nucleicos formados por nucleótidos. As bases nitroxenadas dos seus nucleótidos poden establecer pontes de hidróxeno coas que están en fronte, pero só son posibles determinadas combinacións: G con C, T do ADN con A do ARN, e A do ADN con U do ARN. Estas combinacións constitúen a complementariedade de bases.
Durante a transcrición un encima ARN polimerase le a secuencia dun tramo (xene) dunha das fibras do ADN e crea unha copia complementaria e antiparalela en ARN. As bacterias só teñen unha ARN polimerase, que transcribe todos os tipos de ARN; os eucariotas teñen tres: ARN polimerase I (sintetiza ARNr menos o de 5S), ARN polimerase II (sintetiza ARNm) e ARN polimerase III (sintetiza ARNt e o ARNr 5S).
A transcrición pode explicarse facilmente considerando que comprende 4 ou 5 procesos, durante os cales os encimas e factores proteicos se van movendo sobre o ADN como unha onda. Estes procesos son:
- Os encimas helicases desenrolan a dobre hélice do ADN rompendo as pontes de hidróxeno entre as bases dos seus nucleótidos.
- Os ribonucleótidos do ARN disoltos na célula emparéllanse coas bases complementarias do ADN, ao cal está unido o encima ARN polimerase.
- Fórmase o esqueleto azucre-fosfato do ARN pola acción do encima ARN polimerase, que une ditos nucleótidos entre si. Os nucleótidos chegan á zona en que está tendo lugar a transcrición como nucleósidos trifosfato, pero perden dous fosfatos en forma de pirofosfato e únense ao ARN en formación como nucleótidos monofosfato.
- Rompen as pontes de hidróxeno ARN-ADN liberando a fibra de ARN sintetizada.
- Nas células con núcleo (eucariotas) o ARN é procesado (modificación dos seus extremos, e despois eliminación de intróns) e sae ao citoplasma por un poro nuclear.
O tramo de ADN transcrito a ARN chámase unidade de transcrición e codifica polo menos un xene. A molécula de ARN orixinada chámase transcrito de ARN. O transcrito pode ser un ARNm que vai ser traducido a proteínas ou un ARN que non é traducido, como os ARNr, ARNt e outros ARN pequenos. Nos transcritos de ARNm hai tanto zonas codificantes coma non codificantes (intróns, UTR) con secuencias regulatorias.
A transcrición ten tamén mecanismos de corrección de erros, pero non son tan efectivos como os que actúan durante a replicación do ADN, polo que a fidelidade da copia non é tan grande.[2]
Durante a transcrición o ADN é lido en dirección 3' → 5', polo que o ARN transcrito crece en dirección 5' → 3' (antiparalelismo) e é unha molécula monocatenaria sintetizada de forma "continua" (non hai necesidade de que se formen fragmentos de Okazaki, como sucede nunha das fibras do ADN durante a súa replicación). Só se transcribe unha das dúas cadeas do ADN, chamada cadea molde. A outra cadea do ADN denomínase cadea codificante, porque, aínda que non é a que se copia, é a que ten a mesma secuencia ca o ADN transcrito (excepto que ten timina en vez de uracilo).
A transcrición pode dividirse en 3 fases: iniciación, elongación e terminación.
Transcrición nas bacterias
[editar | editar a fonte]A transcrición ten lugar no citoplasma bacteriano, onde se atopan a gran molécula de ADN da bacteria e os plásmidos. Distinguiremos as fases de iniciación, elongación e terminación.
A iniciación efectúase sobre o promotor, situado antes da secuencia codificante. A ARN polimerase bacteriana está constituída por 5 subunitdades: dúas subunidades α, unha β, unha β' e unha σ[3]. A subunidade σ recoñece unha secuencia consenso no promotor do xene [4], tipicamente a "caixa de Pribnow" [TATAAT], fíxase sobre o ADN e recruta as outras partes do complexo encimático. Unha vez que a ARN polimerase se situou no seu lugar, a subunidade σ sepárase do complexo e β' asegura a unión ao ADN, formándose o chamado complexo pechado. A ARN polimerase desenrola a continuación a dobre hélice nunha zona de 17 pares de bases arredor súa: é o complexo aberto, que forma unha burbulla desenredada para a transcrición.
A fase de elongación pode comezar e substitúese a subunidade σ que sae do complexo por unha chamada Nus A. O complexo encimático transcribe entón o ARN complementario da cadea de ADN molde. A ARN polimerase cataliza a formación dos enlaces fosfodiéster entre os ribonucleótidos adecuados.
A terminación da transcrición faise ao chegar ao terminador do xene, situado despois da secuencia codificante. As secuencias de ADN ricas en pares G-C que hai alí, con 3 pontes de hidróxeno (máis fortemente unidas), ralentizan a progresión da ARN polimerase, e ademais fórmase un bucle en forquita entre dúas rexións complementarias no ARN que bloquea o encima. Finalmente unha proteína de terminación (Rho) libera a molécula de ARN [5].
O ARNm transcrito é directamente utilizable pola maquinaria celular para ser traducido. Como a transcrición e a tradución teñen lugar no mesmo compartimento celular, é mesmo posible que os ribosomas comecen a traducir o ARNm antes de que remate totalmente a súa transcrición.
Nas arqueas a transcrición parécese máis á dos eucariotas, pero é moito menos complexa [6][7][8][9].
Transcrición nos eucariotas
[editar | editar a fonte]Hai numerosas diferenzas entre a transcrición de eucariotas e procariotas. Nos eucariotas a transcrición ten lugar no núcleo celular. A cromatina debe previamente descompactarse para permitir á maquinaria proteica acceder ao ADN. A diferenza do que sucede en procariotas, o ARN producido pola transcrición non é directamente utilizable polos ribosomas e deberá sufrir unha maduración postranscricional.
Os eucariotas teñen tres tipos distintos de ARN polimerases. Pero as polimerases non poden por si soas facer a transcrición, e deben ser axudadas por unha serie de factores de transcrición proteicos. Estes factores denomínanse TFI, TFII, TFIII… e forman un complexo proteico constituído por de 8 a 14 subunidades.
Transcrición realizada pola ARN polmerase II
[editar | editar a fonte]Na transcrición eucariótica dos ARNm distínguense tres fases distintas: iniciación, elongación e terminación. Ao final, o transcrito debe sufrir unha maduración.
Na fase de iniciación o equivalente da «caixa de Pribnow» dos procariotas é nos eucariotas a «caixa TATA», situada uns 30 pares de bases antes da orixe de transcrición. Esta secuencia xoga un papel fundamental porque nela se vai fixar a ARN polimerase II (para transcribir ARNm). Hai outras dúas secuencias ou «caixas» que forman parte das secuencias consenso, entre elas: a caixa CAAT (situada a uns 70 pares de bases antes do sitio de iniciación da transcrición), que é un sitio modulador da transcrición, e a caixa GC. Por último, a maior distancia existen rexións chamadas amplificadores ou intensificadores (enhancers) que poden estimular a transcrición, situados a varios centos de pares de bases do lugar da transcrición, pero que en determinados momentos poden quedar moi próximos ao lugar de transcrición porque o ADN se curva.
Para que se forme o complexo de iniciación primeiro deben unirse os factores proteicos e despois a ARN polimerase. A construción do complexo de iniciación comeza coa proteína TFII D que está constituída pola proteína de unión á TATA ou TBP, que se vai fixar na caixa TATA, o que vai constituír o núcleo do complexo de iniciación.
Despois, os diferentes factores de transcrición ensámblanse sonbre o "núcleo" do complexo. O TFII A estabiliza o complexo TFII D-ADN, o TFII B e o TFII E únense ao ADN, despois únese o TFII F, que é unha helicase dependente do ATP, e por último únese a ARN polimerase II. Este complexo aínda non pode iniciar a transcrición a unha velocidade significativa. Son necesarios factores de transcrición adicionais. Entre eles o CTF (NF1), que se une á caixa CAAT, e o Sp 1, que se une ás caixas GC, que se denominan trans-activadores.[10][11] Ademais, as secuencias amplificadoras (enhancers, «cis activadores») son activadas por proteínas activadoras. Fórmase un bucle no ADN que fai que as zonas amplificadoras, que estaban a bastante distancia, queden ao lado da caixa TATA, de modo que as proteínas activadoras situadas sobre os amplificadores (enhancers) quedan en contacto coa caixa TATA.
A elongación pode entón comezar. O fenómeno central da elongación é a fosforilación do dominio CTD (Dominio Carboxi Terminal), da subunidade de 220 kDa da ARN polimerase II. É un dominio rico en serina e en treonina, que son dous aminoácidos que poden ser fosforilados nos seus grupos -OH. A fosforilación do dominio CTD polo TFII H (unha proteína quinase dependente de ATP) causa que a ARN polimerase se desprace ata o sitio de inicio da transcrición. A adición secuencial de ribonucleótidos para fabricar o transcrito de ARN pode xa comezar. A ARN polimerase comproba que os ribonucleótidos forman as pontes de hidróxeno correctas (emparellamento de bases correcto) e úneos por enlace fosfodiéster.
A terminación está determinada por secuencias sinal específicas, como o sinal de poliadenilación AAUAAA. A polimerase continúa a súa transcrición ata un pouco máis adiante desa secuencia e despois libérase pola acción de diversos factores. A transcrición propiamente dita está xa rematada, pero o ARN obtido non é aínda funcional e debe sufrir unha maduración.
Durante a maduración o extremo 3' do ARN é escindido no sinal de poliadenilación e unha polimerase específica (a poliA polimerase ou PAP) engade moitos residuos de adenina (50 nos lévedos e 200 nos eucariotas superiores) formando a cola poli-A (que non estaba codificada no ADN), que lle dá estabilidade á molécula. No extremo 5' engádese unha carapucha de metilguanosina, que é necesaria para o recoñecemento do ARN durante a tradución nos ribosomas. A última fase da maduración é a eliminación dos intróns, zonas non codificantes características dos eucariotas, intercaladas na rexión codificante do xene. Esta eliminación denomínase splicing do ARN, realizado por un complexo nucleoproteico chamado espliceosoma. Agora o ARNm está listo para ir ao citoplasma e ser traducido.
Transcrición realizada pola ARN polimerase I
[editar | editar a fonte]A ARN polimerase I eucariótica realiza a transcrición da maior parte do ARNr. Primeiramente transcribe unha gran molécula de ARNr 45S, que despois se escinde nos tres ARNr de 28, 18 e 5,8S. O xene do ARNr de 45S atópase nunhas zonas dos cromosomas 13, 14, 15, 21 e 22 humanos chamadas organizadores nucleolares. En cada un destes cromosomas hai unhas 40 copias do xene. O nucléolo orixínase pola transcrición intensa nestes xenes. Nos xenes do ARNr 45S, o recoñecemento da caixa TATA non se pode facer directamente. Cómpre primeiro recoñecer outras dúas zonas de consenso: o promotor central arredor da posición +1 e a secuencia chamada UCE (upstream control element). O factor UBFI recoñece a UCE, o que provoca a curvatura do ADN. Deste modo, a caixa TATA pode ser recoñecida pola proteína de unión á TATA (TBP) e os tres factores TAFI de SLI. A ARN polimerase I é recrutada nese momento e pode comezar a facer a transcrición directamente (sen necesidade do CTD coma no caso do ARNm). Esta síntese detense bruscamente cando se chega ás secuencias de terminación.
Transcrición realizada pola ARN polimerase III
[editar | editar a fonte]A ARN polimerase III eucariótica transcribe os xenes dos ARNt, do ARNr 5S e doutros ARN pequenos, que están espallados polo xenoma. Os mecanismos son diferentes para cada un dos casos, pero a súa particularicdade principal é que posúen promotores internos, é dicir, situados despois da posición +1.
- Os xenes dos ARNt posúen dúas secuencias consenso: as caixas A e B, que son recoñecidas polo factor TFIIIC. Despois pode fixarse o TFIIIB coa súa proteína de unión á TATA (TBP) e os seus dous factores TAFIII. Recrútase a continuación a ARN polimerase III. Entón o TFIIIC deslígase e a síntese pode comezar.
- Os xenes dos ARNr 5S posúen unha caixa C recoñecida polo TFIIIA. Fíxanse seguidamente TFIIIC e B. Recrútase a ARN polimerase e deslíganse os factores TFIIIA e C. A síntese xa pode comezar.
- Na transcrición dos ARN pequenos utilízanse diversos factores intermediarios que permiten a fixación de TAFIII e da TBP de TFIIIB. Recrútase a polimerase e a síntese principia.
Reversotranscrición
[editar | editar a fonte]- Artigo principal: Reversotranscrición.
A reversotranscrición consiste en facer unha copia complementaria de ADN tomando como molde un ARN. É o contrario da transcrición e un proceso moi diferente no que interveñen outros encimas. Mencionámolo aquí porque ten un nome parecido, pero debe ser tratado noutro artigo. Poden facela os encimas dos retrovirus (reversotranscriptase) e certos encimas eucarióticos (telomerase, retrotransposóns).
Notas
[editar | editar a fonte]- ↑ MedicineNet.com. "Transcription definition". Arquivado dende o orixinal o 05 de xuño de 2011. Consultado o 11 October 2009.
- ↑ Berg J, Tymoczko JL, Stryer L (2006). W. H. Freeman, ed. Biochemistry (6th ed.). San Francisco. ISBN 0716787245.
- ↑ Biosynthèse de l'ARN chez les eucaryotes, procaryotes et virus à ARN : Transcription chez les procaryotes Arquivado 15 de outubro de 2009 en Wayback Machine., cours de Vincent Masson
- ↑ Raven Peter H. (2011). McGraw-Hill - New York, ed. Biology: ninth edition. pp. 278–301. ISBN 9780073532226.
- ↑ Richardson J. Rho-dependent termination and ATPases in transcript termination. Biochimica et Biophysica Acta (BBA) - Gene Structure and Expression. 2002;1577(2):251-260. Available at: http://dx.doi.org/10.1016/S0167-4781(02)00456-6 [Accessed March 5, 2011].
- ↑ Littlefield, O., Korkhin, Y., and Sigler, P.B. (1999). "The structural basis for the oriented assembly of a TBP/TFB/promoter complex". PNAS 96 (24): 13668–13673. PMC 24122. PMID 10570130. doi:10.1073/pnas.96.24.13668.
- ↑ Hausner, W; Thomm, M (2001). "Events during Initiation of Archaeal Transcription: Open Complex Formation and DNA-Protein Interactions". Journal of Bacteriology 183 (10): 3025–3031. PMC 95201. PMID 11325929. doi:10.1128/JB.183.10.3025-3031.2001.
- ↑ Qureshi, SA; Bell, SD; Jackson, SP (1997). "Factor requirements for transcription in the archaeon Sulfolobus shibatae". EMBO Journal 16 (10): 2927–2936. PMC 1169900. PMID 9184236. doi:10.1093/emboj/16.10.2927.
- ↑ Mohamed Ouhammouch, Robert E. Dewhurst, Winfried Hausner, Michael Thomm, and E. Peter Geiduschek (2003). "Activation of archaeal transcription by recruitment of the TATA-binding protein". Proceedings of the National Academy of Sciences of the United States of America 100 (9): 5097–5102. PMC 154304. PMID 12692306. doi:10.1073/pnas.0837150100.
- ↑ Seth R. Goldman, Richard H. Ebright, Bryce E. Nickels. Direct Detection of Abortive RNA Transcripts in Vivo. Science 15 May 2009. Vol. 324 no. 5929 pp. 927-928. DOI 10.1126/science.1169237. [1]
- ↑ Dvir A. Promoter escape by RNA polymerase II. Biochim Biophys Acta. 2002 Sep 13;1577(2):208-223. PMID 12213653
Véxase tamén
[editar | editar a fonte]Outros artigos
[editar | editar a fonte]Ligazóns externas
[editar | editar a fonte]- YouTube.com Vídeo explicativo da transcrición en eucariotas (en inglés).
- Interactive Java simulation of transcription initiation.From Center for Models of LifeArquivado 22 de xullo de 2011 en Wayback Machine. at the Niels Bohr Institute.
- Interactive Java simulation of transcription interference--a game of promoter dominance in bacterial virus.From Center for Models of Life at the Niels Bohr Institute.
- Biology animations about this topic under Chapter 15 and Chapter 18
- Virtual Cell Animation Collection, Introducing Transcription Arquivado 14 de abril de 2021 en Wayback Machine.
[[CategoArquivado 26 de agosto de 2011 en Wayback Machine.ría:ÁcidosArquivado 26 de agosto de 2011 en Wayback Machine.nucleicos]]

